Assemblages Macro-Moléculaires
Ce cours a comme objectif la présentation des aspects structuraux spécifiques aux assemblages macromoléculaires et aux demarches expérimentales pour les caracteriser. Le cours décrit des aspects pertinants de la structure des assemblages tels que la morphoologie, la stabilité relative des assemblages, les caracteristiques des surfaces d'interaction entre monomères, les relations de symmétrie, etc. Au delà d'un rappel sur les démarches de biologie structurale sous-jacentes, le cours fait la présentation de différents assemblages de référence, qui permettent d'illustrer la diversité des interactions et l'illustration de caractéristiques communement trouvées dans ces structures. Des interventions par des chercheurs et par les étudiants suivant le cours permettent d'aborder différentes thématiques structurales.
- Introduction
- Taille des Protein Protéines: Oligomerisation; Symétrie; Propriétés de Surface
- Méthodes d'Analyse Structurale; Comparaison Cristallographie+RMN+Microscope Electronique; Notion de Tomographie; Multi-résolution
- Protéines Désordonnées (SL)
- Examples d'Assemblages: Assemblages Viraux et leurs Relations Structure-Fonction
- Examples d'Assemblages: Clatherine; Dynamine; Cytoskelette; Moteurs Moléculaires; Etc
- Présentations d'Articles par les Etudiants
- TP: Introduction pratique à la Cryo-microscopie (Préparation de Grilles; 1ère analyse d'Images)
- 선생님: JONES Rhian
- 선생님: MALDONADO COUTINHO Pedro
- 선생님: PTCHELKINE Denis
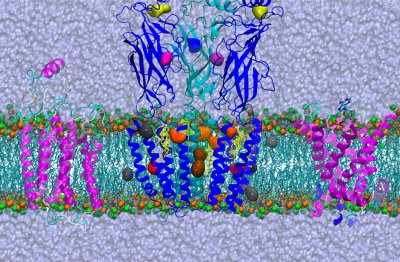
Modélisation moléculaire - JP Duneau (6H cours-TD + 6H TP)
-Mécanique moléculaire et champs de forces
-Modélisation basée sur les connaissances
-Modélisations ab initio
Diffusion moléculaire et modélisation - A. Sergé (6H cours-TD)
Docking moléculaire et drug design - S. Betzi (6H cours-TD + 6H TP)
- 선생님: BETZI Stephane
- 선생님: DUNEAU Jean pierre
- 선생님: SERGE Arnauld
- 선생님: BAFFERT Carole
- 선생님: BRUGNA Myriam
- 선생님: DEMENTIN Sebastien
- 선생님: DUNEAU Jean pierre
- 선생님: ETIENNE Emilien
- 선생님: GRIMALDI Stephane
- 선생님: GUIGLIARELLI Bruno
- 선생님: MARTINHO Marlene
- 선생님: MILEO Elisabetta
- 선생님: PILET Eric
- 선생님: STURGIS James
Dynamique des réseaux d'intéractions moléculaires
- Approches biochimiques
- Co-évolutions et approches théoriques
Dynamique enzymatique
- Réaction à 2 substrats (enz. Formelle)
- Etat prestationnaire (Stop flow et temp. Jump, relaxation cinétique)
- Effets isotopiques (y compris mécanismes)
- Régulation
Dynamique et thermodynamique
- FRAP, FCS
- EPR et marquage de spin
- Protéines Intrinséquement Désordonnées
Simulations
- Relation structure-dynamique fonction
- Champs de forces
- Principes et mise en œuvre
- TP de simulation de dynamique moléculaire
- 선생님: BREUZARD Gilles
- 선생님: BRUGNA Myriam
- 선생님: DUNEAU Jean pierre
- 선생님: KREUZER Corinne
- 선생님: MARTINHO Marlene
- 선생님: PILET Eric
- 선생님: STURGIS James